Texto para a questão sobre PCR em tempo real:
Na reação em cadeia da polimerase (PCR) tradicional, a análise da região de DNA amplificada ocorre após 30-40 ciclos, e o produto é analisado através da eletroforese.
A vantagem da PCR em tempo real é que o processo pode ser monitorado durante a reação. À extensão da amplificação do DNA pode ser determinada após cada ciclo de PCR.
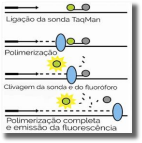
Vários métodos diferentes foram desenvolvidos para isso. O princípio de uma das técnicas mais populares (reação TaqMan) é descrito no experimento seguinte:
Um tumor foi removido da mama de uma paciente. Os DNAs genômicos foram isolados do tumor e do tecido normal circundante, e a reação de PCR foi realizada usando quantidades idênticas das duas amostras de DNA.
As misturas de reação de PCR continham os seguintes componentes:
• amostras de DNAs genômicos;
• muitas cópias de dois primers especificos para uma região do gene HER2;
• muitas cópias de uma sonda TaqMan, um oligonucleotideo que se liga a uma das cadeias moldes na região flanqueada pelos dois primers. Umcorante fluorescente de reportagem, o fluoróforo, é unido à molécula na extremidade 5', e uma molécula extintora é unida a extremidade 3' da sonda, inibindo a fluorescência do corante;
• Tag polimerase;
• trifosfatos de desoxirribonucleosideos (dATP, dGTP, dCTP, dTTP).
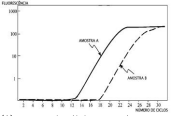
Os gráficos mostram os resultados das amostras À e B da PCR em tempo real realizado em uma paciente com câncer de mama
(A) amostra de células cancerigenas
(B) amostra de células normais.
A fluorescência da amostra A aumentou com maior velocidade, pois: